基因图位克隆的策略与途径(拟南芥)

拟南芥基因克隆的策略与途径
拟南芥(Arabidopsis thaliana)是一种模式植物,具有基因组小(125 Mb p)、生长周期短等特点,而且基因组测序已经
完成(The Arabidopsis Genomic Initiative, 2000)。同时,拟南芥属十字花科(Cruciferae),具有高等植物的一般特点,
拟南芥研究中所取得成果很容易用于其它高等植物包括农作物的研究,产生重大的经济效益,特别是十字花科中还有许
多重要的经济作物,与人类的生产生活密切相关,因此目前拟南芥的研究越来越多地受到国际植物学及各国政府的重视。
基因(gene)是遗传物质的最基本单位,也是所有生命活动的基础。不论要揭示某个基因的功能,还是要改变某个基因的功能,
都必须首先将所要研究的基因克隆出来。特定基因的克隆是整个基因工程或分子生物学的起点。本文就基因克隆的几种
常用方法介绍如下。
1、图位克隆
Map-based cloning, also known as positional cloning, first proposed by Alan Coulson of the University of Cambridge in 1986, Gene isolated by this method is based on functional genes in the genome has a relatively stable loci, in the use of genetic linkage analysis or chromosomal abnormalities of separate groups will queue into the chromosome of a specific location, By constructing high-density molecular linkage map, to find molecular markers tightly linked with the aimed gene, continued to narrow the candidate region and then clone the gene and to clarify its function and biochemical mechanisms.
图位克隆(map-based clonig)又称定位克隆(positoinal cloning),1986年首先由剑桥大学的Alan Coulson提出。用该方法分离基因是根据功能基因在基因组中都有相对较稳定的基因座,在利用分离群体的遗传连锁分析或染色体异常将基因伫到染色体的1个具体位置的基础上,通过构建高密度的分子连锁图,找到与目的基因紧密连锁的分子标记,不断缩小候选区域进而克隆该基因,并阐明其功能和生化机制。
用该方法分离基因是根据目的基因在染色体上的位置进行的,无需预先知道基因的DNA序列,也无需预先知道其表达产物的有关信息。它是通过分析突变位点与已知分子标记的连锁关系来确定突变表型的遗传基础。近几年来随着拟南芥基因组测序工作的完成,各种分子标记的日趋丰富和各种数据库的完善,在拟南芥中克隆一个基因所需要的努力已经大大减少了(图1)。
目前完成整个拟南芥的图位克隆过程大约需要一年时间。在这个过程中,我们从筛选突变体开始,逐渐找到和表型相关的基因。这和反向遗传学(reverse genetics)的方法正好相
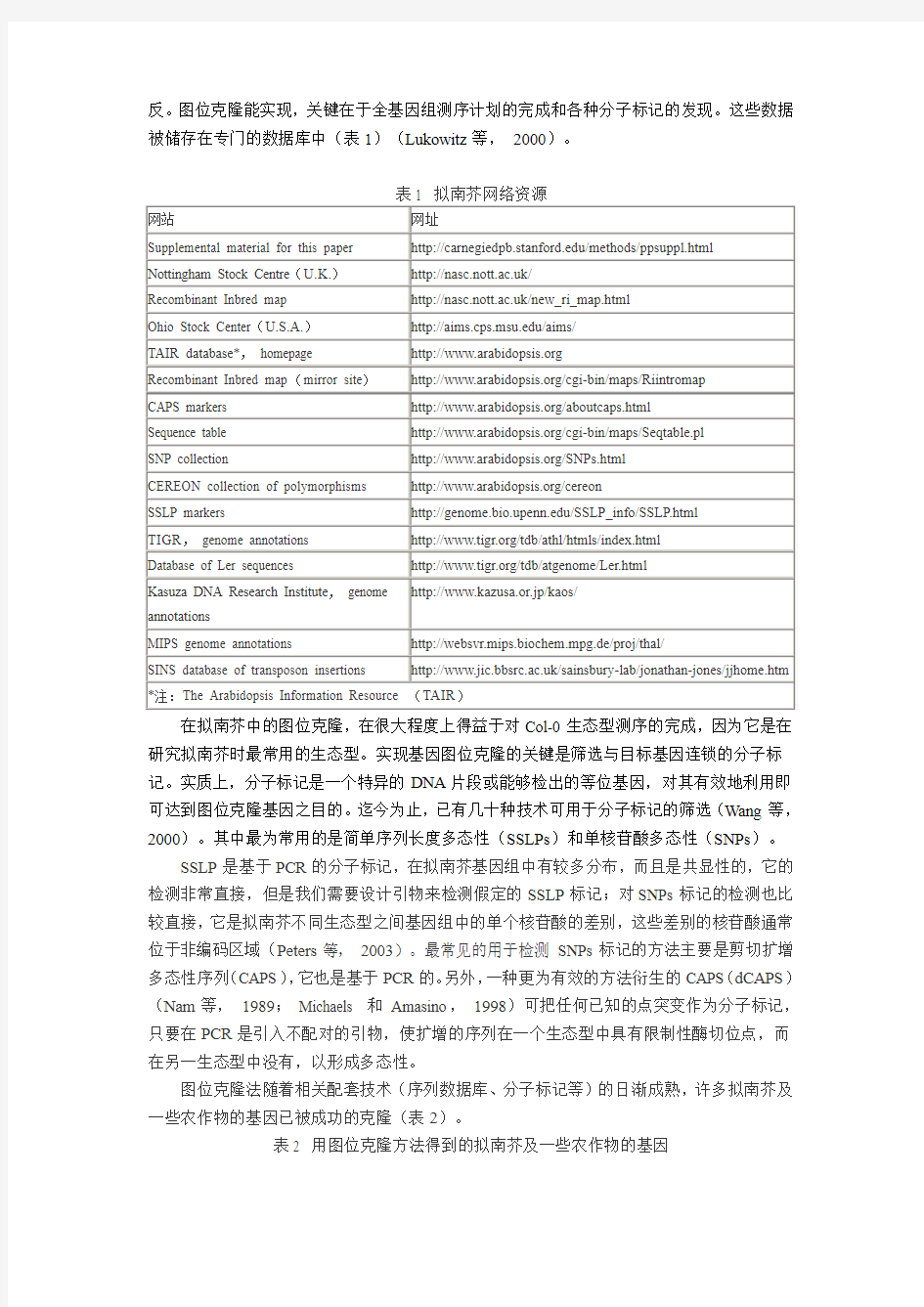
反。图位克隆能实现,关键在于全基因组测序计划的完成和各种分子标记的发现。这些数据被储存在专门的数据库中(表1)(Lukowitz等,2000)。
在拟南芥中的图位克隆,在很大程度上得益于对Col-0生态型测序的完成,因为它是在研究拟南芥时最常用的生态型。实现基因图位克隆的关键是筛选与目标基因连锁的分子标记。实质上,分子标记是一个特异的DNA片段或能够检出的等位基因,对其有效地利用即可达到图位克隆基因之目的。迄今为止,已有几十种技术可用于分子标记的筛选(Wang等,2000)。其中最为常用的是简单序列长度多态性(SSLPs)和单核苷酸多态性(SNPs)。
SSLP是基于PCR的分子标记,在拟南芥基因组中有较多分布,而且是共显性的,它的检测非常直接,但是我们需要设计引物来检测假定的SSLP标记;对SNPs标记的检测也比较直接,它是拟南芥不同生态型之间基因组中的单个核苷酸的差别,这些差别的核苷酸通常位于非编码区域(Peters等,2003)。最常见的用于检测SNPs标记的方法主要是剪切扩增多态性序列(CAPS),它也是基于PCR的。另外,一种更为有效的方法衍生的CAPS(dCAPS)(Nam等,1989;Michaels 和Amasino,1998)可把任何已知的点突变作为分子标记,只要在PCR是引入不配对的引物,使扩增的序列在一个生态型中具有限制性酶切位点,而在另一生态型中没有,以形成多态性。
图位克隆法随着相关配套技术(序列数据库、分子标记等)的日渐成熟,许多拟南芥及一些农作物的基因已被成功的克隆(表2)。
表2 用图位克隆方法得到的拟南芥及一些农作物的基因
本文拟对图位克隆的研究进展做一介绍,以期对植物遗传育种和分子生物学研究有所帮助。
2 图位克隆的一般过程
因为有了拟南芥的基因组序列和高密度的遗传标记,图位克隆过程就变得相对直接。图2例举了一种高效的拟南芥图位克隆方法。从基于Col-0和L er遗传背景的突变体出发,我们有可能在大约一年时间内找出与这个突变相关的基因,这其中主要耗时间的是五个植物(拟南芥)的生长周期(我们假定每个周期为两个月)。
作为作图过程的第一步,突变体植株将和另外一个生态型(Col-0或者L er)的植株杂交。在大多数情况下,用于杂交的突变体植株是作为父本还是母本是没有关系的。然后播种F1代种子。在F1代植物的生长过程中,我们就有可能来对其表现型和基因型进行分析。F1代植物的表型的出现或者消失将显示着我们所研究的突变是显性的还是隐性的。最好通过对一些标记的分析来确认F1代植物是杂合体,而且在杂交过程中我们没有犯错误。当然也有必要确认原来的生态型背景。
图2 图位克隆过程示意图(Jander等,2002)
F1代植物自交得到F2代种子,大约播种600个个体以进行突变基因的粗定位(first-pass mapping,图2)。在其生长过程中,我们可确定其表型,大约有150个个体被认为是纯合体(在隐性突变的情况下是纯合突变体,在显性突变的情况下是纯合野生型)。然后从这150个个体的叶子或者其它组织中制备DNA用于基因型分析。起先用分布于拟南芥五条染色体上的25个标记(相邻的两个标记之间大约相距20 cM)进行分析,确定突变基因是和哪个或者哪几个标记是连锁的,然后用三点测交的方法来定义一个包含突变基因的大约20 cM的遗传间隔。一旦这样的一个遗传间隔被定义之后,接下来的工作就是引入新的标记把这个间隔缩小到大约4 cM。一般来说,利用150个F2代个体是在很大程度上能找到这样一个遗传间隔的,距离突变基因最近的两个分子标记将作为侧面标记而用于下面的进一步分析。
下一步我们将播种一个更大的F2代群体用于突变基因的精细定位(fine-resolution mapping,图2)。最终目标是将包含突变基因的遗传间隔缩小到40 Kb甚至更小(这在拟南芥中大约是0.16 cM)。显然用于作图的F2代植物越多,就越能精确地定位突变基因。一般需要3000~4000个F2代植物个体(包括粗定位时的600个F2代植物个体)来精确地定位突变基因。但是也有很多图位克隆过程用了少于3000个F2代植物个体就成功地定位了突变基因(Lukowitz等,2000)。但是这往往要冒因为作图群体不够大再一次种植F2代植物而延长整个作图过程的时间的风险。
在这个大约4 cM的遗传间隔内找到与突变更紧密连锁的分子标记,一般情况下能在突变两侧找到相距小于40 Kb的两个分子标记。一旦这样的两个分子标记被找到之后,就可以通过测序来找到突变基因。一种有效的方法是设计PCR引物来扩增覆盖这40 Kb的多个重叠的500 bp的片段。将这些片段测序后拼接起来以得到整个40 Kb的序列,然后将它与野生型植物(Col-0或者L er)的序列进行比对,这就可以找到这个区域中的多个基因。从一系列侯选基因中鉴定基因是定位克隆技术的最后一个关键环节。现在最常用的方法是用含有目标基因的大片段克隆如BAC克隆或YAC克隆去筛选cDNA文库,并查询生物数据信息
库,待找出侯选基因后,把这些侯选基因进行下列分析以确定目标基因:(1)精确定位法检查cDNA是否与目标基因共分离;(2)检查cDNA时空表达特点是否与表型一致;(3)测定cDNA序列,查询数据库,以了解该基因的功能;(4)筛选突变体文库,找出DNA 序列上的变化及与功能的关系;(5)进行功能互补实验,通过转化突变体观察突变体表型是否恢复正常或发生预期的表型变化。功能互补实验是最直接、最终鉴定基因的方法。利用新兴的RNA干扰(RNAi)也可有效地确定目的基因。
同源克隆:生物的种、属之间编码基因序列的同源性高于非编码区的序列,基于此原理,在其他种属同源基因被克隆的前提下,构建cDNA文库或基因组文库,然后用已知分子高保守序列制备同源探针,经标记后从相应的文库中筛选阳性克隆,并经核酸序列分析鉴定所克隆的基因,当然在没有全同源探针的情况下,可以使用部分同源探针来筛选与探针序列相关但不完全相同的基因。
图位克隆
同源克隆
转座子标签
表达序列标签(expressed sequence tags, EST)是从一个随机选择的cDNA克隆进行5′端和3′端单一次测序获得的短的cDNA部分序列, 代表一个完整基因的一部分。
DbEST,database EST 表达序列标签数据库。
1951年Barbara Mclintock首先在玉米中发现了控制元件,后来命名为转座元件或转座子(transposon)。转座子是基因组中一段可移动的DNA序列,可以通过切割、重新整合等一系列过程从基因组的一个位置“跳跃”到另一个位置。这一元件不仅可用于分析生物遗传进化上分子作用引起的一些现象,还为基因工程和分子生物学研究提供了强有力的工具,可以在不了解基因产物的生化性质和表达模式的情况下,分离克隆植物基因,即转座子标签(transposon tagging),又称为转座子示踪法。其原理是利用转座子的插入造成基因突变,以转座子序列为基础,从突变株的基因文库中筛选出带有此转座子的克隆,它必定含有与转座子序列相
邻的突变基因的部分序列,再利用这部分序列从野生型基因文库中获得完整的基因〔1〕。1984年,用转座子标签法首先在玉米中分离了bronze基因,该基因编码了玉米花色素合成途径的关键酶——UDP-葡萄糖类黄3-O-葡萄糖基转移酶〔2〕。此后还利用转座子标签技术分离了许多植物基因。
转座子可以分为两大类:以DNA-DNA方式转座的转座子和反转录转座子(retrotransposon)。第一类转座子可以通过DNA复制或直接切除两种方式获得可移片段,重新插入基因组DNA中。根据转座的自主性,这类元件又可以分为自主转座元件和非自主转座元件,前者本身能够编码转座酶而进行转座,后者则需在自主元件存在时方可转座,以玉米的Ac/Ds体系为例,Ac(Activator)属于自主元件,Ds(Dissociation)则是非自主元件,必需在Ac元件存在下才能转座〔1〕。第二类转座子又称为返座元(retroposon)〔3〕,是近年新发现的由RNA介导转座的转座元件,在结构和复制上与反转录病毒(retrovirus)类似,只是没有病毒感染必须的env基因,它通过转录合成mRNA,再逆转录合成新的元件整合到基因组中完成转座,每转座1次拷贝数就会增加1份,因此它是目前所知高等植物中数量最大的一类可活动遗传成分。目前共发现了3种类型反转录转座子:
Tyl-copia类,Ty3-gypsy类和LINE(long interspersed nuclear Clements)类转座子,前两类是具有长末端重复的转座子,LINE类转座子没有长末端重复。高等植物中的反转录转座子主要属于Tyl-copia类,分布十分广泛,几乎覆盖了所有高等植物种类〔4〕。
克隆转座子主要有两条途径:其一,利用抗体识别或cDNA探针从野生型植株中获得表达量降低或不稳定基因座的序列,再从突变体中分离得到相应的转座子:其二是根据序列同源性,在基因组的不同位置分离同一家族的转座子成员。目前已经克隆的植物转座子约156种(来自Genbank的报告
【高中生物】功能基因的克隆及生物信息学分析
(生物科技行业)功能基因的克隆及生物信息学分析
功能基因的克隆及其生物信息学分析 摘要:随着多种生物全基因组序列的获得,基因组研究正从结构基因组学(structuralgenomics)转向功能基因组学(functionalgenomics)的整体研究。功能基因组学利用结构基因组学研究获得的大量数据与信息评价基因功能(包括生化功能、细胞功能、发育功能、适应功能等),其主要手段结合了高通量的大规模的实验方法、统计和计算机分析技术[1],它代表了基因分析的新阶段,已成为21世纪国际生命科学研究的前沿。功能基因组学是利用基因组测序获得的信息和产物,发展和应用新的实验手段,通过在基因组或系统水平上全面分析基因的功能,使生物学研究从对单一基因或蛋白的研究转向多个基因或蛋白同时进行系统的研究,是在基因组静态的组成序列基础上转入对基因组动态的生物学功能学研究[2]。如何研究功能基因,也成为我们面临的一个课题,本文就克隆和生物信息学分析在研究功能基因方面的应用做一个简要的阐述。 关键词:功能基因、克隆、生物信息学分析。 1.功能基因的克隆 1.1图位克隆方法 图位克隆又称定位克隆,它是根据目标基因在染色体上确切位置,寻找与其紧密连锁的分子标记,筛选BCA克隆,通过染色体步移法逐步逼近目的基因区域,根据测序结果或用BAC、YAC克隆筛选cDNA表达文库寻找候选基因,得到候选基因后再确定目标基因。优点是无需掌握基因产物的任何信息,从突变体开始,逐步找到基因,最后证实该基因就是造成突变的原因。通过图位克隆许多
控制质量性状的单基因得以克隆,最近也有报道某些控制数量性状的主效基因(控制蕃茄果实大小的基因克隆[3]、控制水稻成熟后稻谷脱落基因克隆[4]以及小麦VRN2基因克隆[5]等)也通过图位克隆法获得。 1.2同源序列克隆目的基因 首先根据已知的基因序列设计PCR引物,在已知材料中扩增到该片段,并经克隆测序验证,利用放射性同位素标记或其他非同位素标记该PCR片段作为探针,与待研究材料的cDNA文库杂交,就可以获得该基因cDNA克隆,利用克隆进一步筛选基因组文库,挑选阳性克隆,亚克隆并测序,从中就可以筛选到该基因的完整序列。 1.3结合连锁和连锁不平衡的分析方法 结合连锁和连锁不平衡的分析方法是未知基因克隆研究领域发展的新方向[6]。(Linkagedisequilibrium,LD)。与连锁分析不同,连锁不平衡分析可以利用自然群体中历史发生的重组事件。历史上发生的重组使连锁的标记渐渐分布到不同的同源染色体上,这样就只有相隔很近的标记才能不被重组掉,从而形成大小不同的单倍型片段(Haplotypeblock)。这样经过很多世代的重组,只有相隔很近的基因,才能仍处在相同的原始单倍型片段上,基因间的连锁不平衡才能依然存在。所以基于连锁不平衡分析,可以实现目的基因的精细定位。林木大多为自由授粉的异交物种,所以连锁不平衡程度很低,林木基因组中的LD可能会仅局限于非常小的区域,这就为目的基因的精细定位提供了可能,结合SNP检测技术,科学家甚至可以将效应位点直接与单个的核苷酸突变关联起来,进行数量性状寡核苷酸
基因图位克隆的策略与途径
基因图位克隆的策略与途径 拟南芥(Arabidopsis thaliana)是一种模式植物,具有基因组小(125 Mbp ) 、生长周期短等特点,而且基因组测序差不多完成 (The Arabidopsis Genomic Initiative, 2000)。同时,拟南芥属十字花科(Cruciferae),具有高等植物的一样特点,拟南芥研究中所取得成果专门容易用于其它高等植物包括农作物的研究,产生重大的经济效益,专门是十字花科中还有许多重要的经济作物,与人类的生产生活紧密有关,因此目前拟南芥的研究越来越多地受到国际植物学及各国政府的重视。 基因(gene是遗传物质的最差不多单位,也是所有生命活动的基础。不论 要揭示某个基因的功能,依旧要改变某个基因的功能,都必须第一将所要研究的基因克隆出来。特定基因的克隆是整个基因工程或分子生物学的起点。本文就基因克隆的几种常用方法介绍如下。 1 、图位克隆 Map-based cloning, also known as positional cloning, first proposed b y Alan Coulson of the University of Cambridge in 1986, Gene isolated b y this method is based on functional genes in the genome has a relativel y stable loci, in the use of genetic linkage analysis or chromosomal abnor malities of separate groups will queue into the chromosome of a specific location, By constructing high-density molecular linkage map, to find mole cular markers tightly linked with the aimed gene, continued to narrow the candidate region and then clone the gene and to clarify its function and biochemical mechanisms. 用该方法分离基因是按照目的基因在染色体上的位置进行的,无需预先明白基因的DNA 序列,也无需预先明白其表达产物的有关信息。它是通过分析突变位点与已知分子标记的连锁关系来确定突变表型的遗传基础。近几年来随着拟南芥基因组测序工作的完成,各种分子标记的日趋丰富和各种数据库的完善,在拟南芥中克隆一个基因所需要的努力差不多大大减少了(图1)。
克隆技术简介
克隆技术介绍 张勋学号:160820216 摘要克隆技术是生命科学技术领域里非常重要的部分,随着新时代的到来,克隆技术在人类生产生活中将发挥更加重要的作用。人们享受着克隆技术带来的巨大好处,但与此同时,克隆技术对人类的可持续发展也提出了问题和挑战。本文是通过从实质、方法、应用价值等方面对克隆技术进行一些介绍。 一、克隆技术实质 1963 年J.B.S.Haldane在题为“人类种族在未来二万年的生物可能性”的演讲上采用“克 隆(Clone)”的术语。学家把人工遗传操作动物繁殖的过程叫“克隆”,这门生物技术叫“克隆技术”,其本身的含义是无性繁殖,即由同一个祖先细胞分裂繁殖而形成的纯细胞系,该细胞系中每个细胞的基因彼此相同。早在1938年,德国胚胎学家Speman 最早提出克隆设想。1962年,英国剑桥大学的Gurdon进行了青蛙胚胎核移植,获得成年蛙。在经历半个多世纪的研究后,终于在1996年的7月5日,在苏格兰罗斯林研究所中,随着用体细胞克隆出来的小羊多莉的诞生,哺乳动物克隆技术真正的来到我们面前。克隆技术作为人类在生物科学领域取得的一项重大技术突破,反映了细胞核分化技术、细胞培养和控制技术的进步,它对于扩大良种动物群体,提高畜群的遗传素质和生产能力,拯救濒危动物等的方面而言是迄今为止最为理想手段。 克隆也可以理解为复制,就是从原型中产生出同样的复制品,它的外表及遗传基因与原型完全相同,但大多行为思想不同。时至今日,“克隆”的含义已不仅仅是“无性繁殖”,凡是来自同一个祖先,无性繁殖出的一群个体,也叫“克隆”。这种来自同一个祖先的无性繁殖的后代群体也叫“无性繁殖系”,简称无性系。简单讲就是一种人工诱导的无性繁殖方式。但克隆与无性繁殖是不同的。克隆是指人工操作动物繁殖的过程,无性繁殖是指:不经过两性生殖细胞的结合由母体直接产生新个体的生殖方式。 植物基因的克隆技术是生命科学研究的重要组成部分,是现代生命科学技术中最核心的内容,它是随着20 世纪70 年代初DNA 体外重组技术的发明而发展起来的,其目标是识别和分离特异基因并获得基因完整序列,确定其在染色体上的位置,阐明其生化功能,并利用生物工程手段应用到生产实践中去。一般来讲,基因克隆的策略可分为两种途径:正向遗传学途径和反向遗传学途径。 正向遗传学途径以待克隆的基因所表现的功能为基础,通过鉴定基因的表达产物或表型性状进行克隆,如功能克隆和表型克隆等;反向遗传学途径则着眼于基因本身特定的序列或者在基因组中的特定位置进行克隆,如定位克隆、同源序列法克隆等;随着DNA测序技术和生物信息学的发展,又产生了电子克隆等新兴克隆技术。目前,在玉米,水稻、油菜、拟南芥、烟草、番茄等多种植物中,已经克隆了许许多多与植物的产量、品质、抗性及农艺性状等相关的基因。现对在植物基因克隆过程中运用的主要技术进行综述,以把握植物基因克隆技术的发展历程,并对未来的发展趋势进行展望。
拟南芥的图位克隆技术
拟南芥基因的图位克隆技术 浙江大学生命科学学院徐冰 浙江杭州310029 1 国内外研究现状 拟南芥(Arabidopsis thaliana)是一种模式植物,具有基因组小(125 Mbp)、生长周期短等特点,而且基因组测序已经完成(The Arabidopsis Genomic Initiative, 2000)。同时,拟南芥属十字花科(Cruciferae),具有高等植物的一般特点,拟南芥研究中所取得成果很容易用于其它高等植物包括农作物的研究,产生重大的经济效益,特别是十字花科中还有许多重要的经济作物,与人类的生产生活密切相关,因此目前拟南芥的研究越来越多地受到国际植物学及各国ZF的重视。 从遗传学的观点来看,基因克隆的途径可概括为正向遗传学和反向遗传学两种。正向遗传学途径指的是通过被克隆基因的产物或表现型突变去进行;反向遗传学途径则指的是依据被克隆基因在染色体上的位置来实现。虽然一些模式生物(如拟南芥)的基因组测序已经完成,但还有40%的基因(在拟南芥中)的功能还是未知的。 图1 图位克隆所需努力的比较(1995年和2002年)(Jander等,2002) 图位克隆(map-based cloning)又称定位克隆(positional cloning),1986年首先由剑桥大学的Alan Coulson提出(Coulson等,1986),用该方法分离基因是根据目的基因在染色体上的位置进行的,无需预先知道基因的DNA序列,也无需预先知道其表达产物的有关信息。它是通过分析突变位点与已知分子标记的连锁关系来确定突变表型的遗传基础。近几年来随着拟南芥基因组测序工作的完成,各种分子标记的日趋丰富和各种数据库的完善,在拟南芥中克隆一个基因所需要的努力已经大大减少了(图1)。 目前完成整个拟南芥的图位克隆过程大约需要一年时间。在这个过程中,我们从筛选突变体开始,逐渐找到和表型相关的基因。这和反向遗传学的方法正好相反。图位克隆能实现,关键在于全基因组测序计划的完成和各种分子标记的发现。这些数据被储存在专门的数据库中
基因克隆技术的研究进展_钟军
第6卷第4期(专辑) 2002年12月 生命科学研究 Life Science Research Vol.6No.4(Suppl.) Dec.2002基因克隆技术的研究进展X 钟军,李,官春云 (湖南农业大学油料作物研究所,中国湖南长沙410128) 摘要:为能快速而准确地克隆目的基因,综述了一些基因克隆常用技术,包括差异表达基因分离技术、转座子标签技术、图位克隆技术、同源序列技术、表达序列标签技术的原理、应用及应用潜力,并对其作了简要的评价. 这些技术有利有弊,应根据不同的实验目的和水平来选择相应的技术. 关键词:基因;克隆;差异表达基因分离技术;转座子标签技术;图位克隆技术;同源序列技术;表达序列标签技术 中图分类号:Q78文献标识码:A文章编号:1007-7847(2002)S1-0148-05 Advances in Gene Cloning Technique ZHONG Jun,LI Xun,GUAN Chun-yun (T he Oil Crop Institute of H unan Agriculture University,Chan gsha410128,H unan,China) Abstract:To clone candidate gene quickly and correctly,advances about gene cloning included map-based cloning, transposon tagging,homology-based candidate gene method,expressed sequence tagging methods and some differen-tially expressed gene clone method are introduced and appraised.Because of the advantages and disadvanta ges of those techniques,various technique should be selected according special purpose and level. Key words:gene;clone;differentially e xpressed gene clone method;transposon tagging;map-based cloning;ho-mology-based candidate gene method;e xpressed sequence ta gging method (Li f e Science Research,2002,6(Suppl):148~152) 克隆基因的途径有两种,正向遗传学和反向遗传学途径.前者是依据目标基因所表现的功能为基础,通过鉴定其产物或某种表型突变而进行的;后者则着眼于基因本身,通过特定的序列或在基因组中的位置进行.近几十年来,许多重点实验室致力于植物基因的克隆,到1992年取得了突破性进展.基因的克隆一般采用下列技术:差异表达基因分离技术、转座子标签技术、表达序列标签技术、图位克隆技术和同源序列技术等. 1差异表达基因分离技术 1.1扣除杂交技术 扣除杂交技术的原理是用有特异性表达基因的目标样提取mRNA经逆转录形成cDNA探针,与无特异性表达基因的参照样的过量mRNA或cDNA杂交,经两轮充分杂交后,移去杂交分子和过量的无特异性表达基因的参照样mRNA或cD-NA,将不形成杂交体的有特异性表达基因的目标样cDNA纯化富集、扩增,建立相应cDNA文库即为差异表达基因cDNA文库.此技术最早是由Lamar和Palmer于1984年提出[1],他们先用超声波打断雌性小鼠的DNA,用Mbo1完全消化雄性小鼠DNA;将两者一起变性、复性,再将产物克隆入表达载体的Bam H I位点中,只有那些两端有GATC序列的基因才能被克隆入载体,这样就达到了扣除两者共有序列的目的,并得到雄性小鼠 X收稿日期:2002-06-11;修回日期:2002-10-14 作者简介:钟军(1973-),女,湖南沅江人,博士研究生,从事分子遗传学研究.Tel:+86-0731-*******,E-mail:zhhjp@s https://www.wendangku.net/doc/915469610.html,
植物基因克隆的策略与方法
植物基因克隆的策略与方法 基因的克隆就是利用体外重组技术,将特定的基因和其它DNA顺序插入到载体分子中。基因克隆的主要目标是识别、分离特异基因并获得基因的完整的全序列,确定染色体定位,阐明基因的生化功能,明确其对特定性状的遗传控制关系。通过几十年的努力由于植物发育,生理生化,分子遗传等学科的迅速发展,使人们掌握了大量有关植物优良性状基因的生物学和遗传学知识,再运用先进的酶学和生物学技术已经克隆出了与植物抗病、抗虫、抗除草剂、抗逆,育性、高蛋白质及与植物发育有关的许多基因。我们实验室对天麻抗真菌蛋白基因作了功能克隆的研究(舒群芳等,1995;舒群芳等,1997),为了克隆植物基因也探讨了其它克隆方法,本文论述基因克隆的策略、方法及取得的一些进展。 1 功能克隆(functional Cloning) 功能克隆就是根据性状的基本生化特性这一功能信息,在鉴定和已知基因的功能后克隆(Collis,1995)。其具体作法是:在纯化相应的编码蛋白后构建cDNA文库或基因组文库,DNA文库中基因的筛选根据情况主要可用二种办法进行,(1)将纯化的蛋白质进行氨基酸测序,据此合成寡核苷酸探针从cDNA库或基因组文库中筛选编码基因,(2)将相应的编码蛋白制成相应抗体探针,从cDNA入载体表达库中筛选相应克隆。功能克隆是一种经典的基因克隆策略,很多基因的分离利用这种策略。 Hain等从葡萄中克隆了两个编码白藜芦醇合成的二苯乙烯合成酶基因(Vst1和Vst2),葡萄中抗菌化合物白藜芦醇的存在,可以提高对灰质葡萄孢(Botrytis cinerce)的抗性,在烟草和其它一些植物中无二苯乙烯合成酶,因此
基因图位克隆的策略与途径拟南芥
基因图位克隆的策略与途 径拟南芥 Ting Bao was revised on January 6, 20021
拟南芥基因克隆的策略与途径 拟南芥(Arabidopsis thaliana)是一种模式植物,具有基因组小(125 Mbp)、生长周期短等特点,而且基因组测序已经完成(The Arabidopsis Genomic Initiative, 2000)。同时,拟南芥属十字花科(Cruciferae),具有高等植 物的一般特点,拟南芥研究中所取得成果很容易用于其它高等植物包括农作物的研究,产生重大的经济效益,特别是 十字花科中还有许多重要的经济作物,与人类的生产生活密切相关,因此目前拟南芥的研究越来越多地受到国际植物 学及各国政府的重视。 基因(gene)是遗传物质的最基本单位,也是所有生命活动的基础。不论要揭示某个基因的功能,还是要改变某个基因的 功能,都必须首先将所要研究的基因克隆出来。特定基因的克隆是整个基因工程或分子生物学的起点。本文就基因克隆 的几种常用方法介绍如下。 1、图位克隆 Map-based cloning, also known as positional cloning, first proposed by Alan Coulson of the University of Cambridge in 1986, Gene isolated by this method is based on functional genes in the genome has a relatively stable loci, in the use of genetic linkage analysis or chromosomal abnormalities of separate groups will queue into the chromosome of a specific location, By constructing high-density molecular linkage map, to find molecular markers tightly linked with the aimed gene, continued to narrow the candidate region and then clone the gene and to clarify its function and biochemical mechanisms.图位(map-based clonig)又称克隆(positoinal cloning),1986年首先由剑桥大学的Alan Coulson提出。用该方法分离基因是根据功能基因在中都有相对较稳定的基因座,在利用分离群体的遗传连锁分析或将基因伫到染色体的1 个具体位置的基础上,通过构建高密度的分子连锁图,找到与目的基因紧密连锁的分子标记,不断缩小候选区域进而克隆该基因,并阐明其功能和生化。 用该方法分离基因是根据目的基因在染色体上的位置进行的,无需预先知道基因的DNA序列,也无需预先知道其表达产物的有关信息。它是通过分析突变位点与已知分子标记的连锁关系来确定突变表型的遗传基础。近几年来随着拟南芥基因组测序工作的完成,各种分子标记的日趋丰富和各种数据库的完善,在拟南芥中克隆一个基因所需要的努力已经大大减少了(图1)。
功能基因的克隆及生物信息学分析
功能基因的克隆及其生物信息学分析 摘要:随着多种生物全基因组序列的获得,基因组研究正从结构基因组学(structural genomics)转向功能基因组学(functional genomics)的整体研究。功能基因组学利用结构基因组学研究获得的大量数据与信息评价基因功能(包括生化功能、细胞功能、发育功能、适应功能等),其主要手段结合了高通量的大规模的实验方法、统计和计算机分析技术[1],它代表了基因分析的新阶段,已成为21世纪国际生命科学研究的前沿。功能基因组学是利用基因组测序获得的信息和产物,发展和应用新的实验手段,通过在基因组或系统水平上全面分析基因的功能,使生物学研究从对单一基因或蛋白的研究转向多个基因或蛋白同时进行系统的研究,是在基因组静态的组成序列基础上转入对基因组动态的生物学功能学研究[2]。如何研究功能基因,也成为我们面临的一个课题,本文就克隆和生物信息学分析在研究功能基因方面的应用做一个简要的阐述。 关键词:功能基因、克隆、生物信息学分析。 1.功能基因的克隆 1.1 图位克隆方法 图位克隆又称定位克隆,它是根据目标基因在染色体上确切位置,寻找与其紧密连锁的分子标记,筛选BCA克隆,通过染色体步移法逐步逼近目的基因区域,根据测序结果或用BAC、YAC克隆筛选cDNA表达文库寻找候选基因,得到候选基因后再确定目标基因。优点是无需掌握基因产物的任何信息,从突变体开始,逐步找到基因,最后证实该基因就是造成突变的原因。通过图位克隆许多控制质量性状的单基因得以克隆,最近也有报道某些控制数量性状的主效基因(控制蕃茄果实大小的基因克隆[3]、控制水稻成熟后稻谷脱落基因克隆[4]以及小麦VRN2 基因克隆[5]等)也通过图位克隆法获得。
图位克隆基因研究进展
图位克隆基因研究进展 宋成标 摘要图位克隆是在不清楚基因产物结构和功能的情况下,根据基因在染色体上都有稳定的基因座实现的。随着各种分子标记技术和高质量基因组文库构建技术的发展,图位克隆现已经成为分离生物体基因的一种常规技术。本文主要概述了图位克隆的一般步骤,包括目的基因的初步定位、精细定位和遗传做图、染色体步行和登陆及利用功能互补实验鉴定目的基因。最后,对图位克隆技术存在的局限和发展前景作了初步的分析。 关键词图位克隆, 分子标记, 精细定位, 基因组文库 Abstract Map-based cloning is based on the functional genes have their particular gene locus on chromosomes,when we know about the structure and function of gene products unclearly.With the rapid development of molecular marker technologies and constructing high quality genomic library technologies, map-based cloning had already become a common bio—technique for gene isolation. This article summarized mainly the processes of the map-based cloning in principle,including first-pass mapping of candidate gene、fine scale-mapping and building genetic map、chromosome walking or landing and finally complement experiment for identifing candidate gene. Finally the problems and the prospects in the map-based cloning are analyzed Keywords Map-based cloning, Molecular marker, Fine maping, Genomic library 从遗传学观点来看,基因克隆有两条途径:正向遗传学途径和反向遗传学途径。正向遗传学途径指的是通过被克隆基因的产物或表型突变去进行,如传统的功能克隆及近年来迅速发展的表型克隆;反向遗传学途径是根据被克隆的目的基因在染色体上都有稳定的位置来实现的。由于在多数情况下,我们并不清楚基因产物的结构和功能,很难通过正向遗传学途径克隆基因,而反向遗传学途径则显示了较好的前景。其中可以利用的主要有三种方法,分别是转座子标签法、随机突变体筛选法和图位克隆法。转座子标签法中受转座子的种类、转座频率及有些植物存在内源转座子等的影响,随机突变体筛选法则随机性较大且不能控制失活基因的种类和数量等,限制了它们的应用。图位克隆(map-based cloning)又称为定位克隆(positional cloning),1986年首先由剑桥大学的Coulson 等提出,用该方法分离基因是根据目的基因在染色体上的位置进行的,无需预先知道基因的DNA序列,也无需预先知道其表达产物的有关信息。它是通过分析突变位点与已知分子标记的连锁关系来确定突变表型的遗传基础。随着模式物种(拟南芥、水稻)全基因组测序的完成,各种分子标记技术的发展促进了高密度分子标记连锁图谱的建立和各种数据库的完善。图位克隆技术越来越成熟,已经成为分离生物基因的一种常规方法。本文将对图位克隆技术的相关策略作一介绍。 1图位克隆的策略 自1992年图位克隆技术首次在拟南芥中克隆到ABI3(Girauda et al., 1992)基因和F AD3 (Arondel et al., 1992)基因以来,图位克隆技术在其它相关技术快速发展的支持下迅速发展起来。它是依据功能基因在生物基因组中都有相对稳定的基因座,在利用分子标记技术对目的基因进行精细定位的基础上,用与目的基因紧密连锁的分子标记筛选已构建的DNA文库(如Cosmid、YAC、BAC等文库),构建出目的基因区域的遗传图谱和物理图谱,再利用此物理图谱通过染色体步行、跳跃或登陆的方式获得含有目的基因的克隆,最后通过遗传转化和功能互补实验来验证所获得的目的基因(图1)。 初步定位(First-pass maping)-------构建遗传图谱(constructing genetic map)-----精细定位(fine maping)---------构建物理图谱( constructing physical map)------染色体步移、登陆(chromosomal walking、landing)-------确定侯选基因(Consider candidate genes)----遗传互补验证目的基因(Through genetic complementation (transformation) to identify candidate gene)(请帮我画一个简易图表,把内容填进去) 图1 图位克隆的主要步骤 Figure 1 Key steps in map-based cloning process
水稻基因的图位克隆技术
水稻基因的图位克隆技术 吴自明 (江西农业大学,作物生理生态与遗传育种教育部重点实验室,农业部双季稻生理生态与栽培重点实验室,江西省作物生理生态与遗 传育种重点实验室,江西南昌330045) 摘要 综述了水稻图位克隆技术的原理、技术环节及其在水稻基因克隆上的应用,分析了当前存在的主要问题,并对其应用前景作出了展望。 关键词 水稻;图位克隆;基因 中图分类号 S 511 文献标识码 A 文章编号 0517-6611(2008)34-14905-02 Map based C lo ning T echnique of R ice Genes WU Zi m ing (Key Laboratory of C rop Ph ysiology,Ecol ogy and Genetic B reeding,Mi nistry of Ed ucation,Key Laboratory of Ph ysiology,Ecology and C ultivati on of Double C roppin g Rice,Mini stry of Agriculture,Key Lab oratory of Crop Physi ology,Ecology an d Genetic Breedin g of Jian gxi Province,Jiangxi Agricultural Uni versi ty,Nanchang,Jiangxi 330045)Abstract The p rinciple an d tech nical links of m ap based gene cloni ng techniq ue i n rice an d its applications in the gene cloni ng of rice were s um ma rized .And the mai n existing problems at present were analyzed .And its applicati on foregrou nd was p redicted.Key w ords Rice;Map based cloni ng;Gene 基金项目 江西省教育厅项目(GJJ09477);江西农业大学博士启动基 金;江西农业大学校自然科学基金。 作者简介 吴自明(1974-),男,江西鄱阳人,副教授,从事植物分子 生物学研究。 收稿日期 2008 10 06 近年来,水稻基因组研究进展非常迅速,高密度遗传图谱和物理图谱的构建,全基因组序列的公布,数以万计ES T 、全长c DN A 等序列及功能分析数据的释放以及新型水稻分子标记及其高效检测技术的发展等,为基因的图位克隆带来了新的思路和方法。同时,这些新的进展也能够使基因的精细定位和物理图谱构建等相关工作大大简化,使基因的图位克隆朝着更加简便、快速的方向发展。1 图位克隆技术原理 图位克隆(Ma p based Cloning)又称定位克隆(Positional Cloning),1986年首先由剑桥大学的Alan Co ulson 提出[1]。用该方法分离基因是根据目的基因在染色体上的位置进行,无需预先知道基因的D N A 序列,也无需预先知道其表达产物的有关信息,而是通过分析突变位点与已知分子标记的连锁关系来确定突变表型的遗传基础。实现基因图位克隆的关键是筛选与目标基因连锁的分子标记。 近几年来,水稻各种分子标记的日趋丰富和各种数据库的日趋完善,在很大程度上得益于以粳稻日本晴和籼稻9311为代表的基因组测序的完成[2-3]。目前已有几十种技术可用于分子标记筛选,其中最常用的是简单序列长度多态性(SSLPs)、单核苷酸多态性(SNPs)和插入缺失多态性(Inser tio n/Deletio n,InDel)[4-7]。Shen 等利用日本晴和9311基因组序列构建了水稻基因组水平的D NA 多态性数据库,其中包括1703176个单核苷酸多态性(Single Nucleo tide Polymor phis m,SNP)和479406个插入缺失多态性(InDel)[8]。Fe ltus 等通过对除去多重拷贝序列及低质量序列后的日本晴和9311基因组草图的比对分析,得到408898个D N A 多态性,包括SNP 和单碱基I nD el [9],这些差别的核苷酸通常位于非编码区[10]。 目前,常把SNP 多态性转化成基于P CR 的剪切扩增多态性(Cle ave d Amplified P olymorphic Se que nc es,CAPS)或CAPS 衍生的dCAPS 标记[11-12]。CAPS 标记是PCR 反应和酶切相结 合产生的一种分子标记。如果不同材料间在PCR 扩增区域有S NP 位点,且该位点是限制性内切酶作用位点,那么不同 材料的PCR 扩增产物经特定的酶切后,再进行琼脂糖凝胶电泳就会表现多态性。当SNP 恰好位于限制性酶切位点比较少时,这种情况可以在CAPS 标记的基础上通过在扩增引物中引入错配碱基,则可以结合SNP 位点引入新的限制性内切酶作用位点,产生和CAPS 标记类似的多态性,这就是dCAPS 的方法。用CAPS 或dCAPS 的方法则可以将几乎所有的SNP 位点转化成以P CR 为基础的分子标记[12] 。 2 图位克隆技术环节 2.1 构建遗传作图群体 对于基因图位克隆而言,构建特殊的遗传作图群体是筛选与目标基因紧密连锁分子标记的关键环节。常用的作图群体有F 2、近等基因系、重组自交系等群体,水稻常用F 2群体。创建F 2群体应注意优先选择基因组已测序的日本晴、9311和培矮64S 等品种为亲本之一。2.2 基因初定位 一般说来,当标记为显性遗传时,欲获得最大遗传信息量的F 2群体,需借助于进一步子代测验,以分辨F 2中的杂合体。为此,Mic helmo re 等发明分离群体分组分析法(Bulke d Se gre ga nt Ana lysis,BS A)以筛选目标基因所在局部区域的分子标记[13]。其原理是将目标基因的F 2(或BC)代分离群体各个体仅以目标基因所控制的性状按双亲表型分为2群,每一群中各个体D N A 等量混合,形成2个D N A 混合池(如抗病和感病、不育和可育),并且用目的基因附近的所有分子标记对混合D NA 样品池进行分析,根据所有池中包含有交换的DN A 池的比例来确定与目的基因连锁最紧密的分子标记和目的基因附近所有分子标记的顺序。混合样品作图可以极大提高分子标记分析效率,减小D NA 提取工作量。 2.3 基因精细定位 一旦把目标基因初步定位在2个标记之间后,就可以从国际水稻基因组测序计划(IRG SP)公布的序列中下载这2个标记区域的部分P AC/BAC 克隆序列。利用软件SSRI T 搜索克隆序列中的微卫星序列,然后选择合适的微卫星序列进行特异PCR 引物的设计。也可以直接借助于公共数据库的序列进行比较,如寻找R GP 基因组数据库(粳稻)与中国华大基因组数据库(籼稻)的单核苷酸多态性(SNP)序列差异,设计CAPS 或dCAPS 标记和插入/缺失多态 安徽农业科学,J ou rn al of An hui Agri.Sci.2008,36(34):14905-14906 责任编辑 张彩丽 责任校对 张士敏
植物基因克隆技术的发展与展望
植物基因克隆技术的发展与展望 摘要:基因克隆技术是生命科学技术领域里非常重要的部分,为了纵览植物基因克隆的理论和技术的发展创新历程.对各种技术体系、正向遗传学途径、反向遗传学途径(包含定位克隆和同源序列克隆及随后发展起来的电子克隆)进行了综述。随着后基因组时代的到来,植物基因克隆技术将发挥更加重要的作用。 关键词:基因克隆、定位克隆、转座子标簦法、基因芯片电子克隆 植物基因的克隆技术是生命科学研究的重要组成部分,是现代生命科学技术巾最核心的内容,它是随着20世纪70年代初DNA体外囊组技术的发明而发展起来的,其目标是识别和分离特异基因并获得基因完整序列,确定其在染色体上的位置,阐明其生化功能,并利用生物T程手段应用到生产实践巾去。一般来讲,基因克隆的策略町分为两种途径:正向遗传学途径和反向遗传学途径。现对在植物基因克隆过程巾运用的主要技术进行综述.以把握植物基因克隆技术的发展历程,并对未来的发展趋势进行展望。 1、定位克隆 定位克隆技术(positional cloning)又叫图位克隆(map—based cloning).是枞据目标基因在染色体上的位置进行基因克隆的一种方法,适合于克隆编码产物未知的基因、其基本原理是根据功能基因在基因组巾存在相对较稳定的基因座,在利用分子标记技术对目的基因进行精确定位的基础上,用与目标基因两侧紧密连锁的分子标记筛选含有大的插入片段的基因组义库(如BAC和YAC).用筛选到的阳性克隆构建目的基因区域的跨叠群,再通过染色体步行(chromosomewalking)逐步逼近候选区域或通过染色体登陆(chro—lnosolne landing)的方法获得含有目标基因的大片段克隆,将含有目标基因的大片段克隆进行亚克隆.或以大片段克隆作探针筛选cDNA义库:从而将目标基因确定在一个较小的DNA片段上并进行序列分析.通过遗传转化和功能互补试验分析,签定获得目的基因【1】。 植物巾运用图位克隆技术,从拟南芥、水稻、番茄、大麦、小麦、甜菜、马铃薯等植物巾分离了几十个重要的基因,并以抗病基因的克隆居多.如番茄的埘基因121.Hero基因;马铃薯的Cpa2基因?,拟南芥的RPW8基因?、PBSI基因?、Rppl3基因?和水稻的Pita、Xal、Pi —b等基因。随着比较基因组研究的兴起.利用同科异种植物问染色体的共线性进行比较作图.如以拟南芥、番茄和水稻为巾介来克隆其他十字花科、茄科和禾本科植物的基因,将成为一个新的发展方向 2、转座子标签法 转座子(Transposon)是口J从染色体的一个位置转移到另一位置的DNA片段,最早在玉米巾发现的.随后的研究表明,在生物界巾转座子是普遍存在的.并在生物的遗传进化方面有重要作用。转座子标签技术克隆基因的基本原理是.利用转座子插入到基因内部或邻近位点,会引起相火表型突变的特点.以转座子的已知序列为标签,克隆因转座子捕入而功能失活的基因,如果某基因的突变是巾于转座子插入而造成的,那么以转座子序列为探针就nr从变异株的基因组巾筛选出带有此转座子的部分基因.再以突变基因的部分序列作探针,即口J从野生型义库巾克隆m完整的基因,在植物中利用转座子的有玉米的Ac/Ds.En/Spm和金鱼草的Tn3等,其中应用最多的是AciDs双因子系统【2】。 利用转座子标记技术目前已克隆y-0的植物抗病基因有玉米抗网斑病基因Hml、Hm2“.番船抗叶霉病基因a之、a4d、cf巧、Cf-9、C}9B及cf一磁P型“。1?.烟草抗花叶病毒病基因
常用的植物目的基因克隆技术
常用的植物目的基因克隆技术 常用的植物目的基因克隆技术 1、通过已知基因产物的分析和鉴定 这类技术主要通过生物化学和病理学研究分离鉴定有关基因的蛋白产物,并对蛋白质氨基酸顺序进行分析,推断出编码该蛋白质的基因序列,然后通过抗体、寡聚核苷酸探针或PCR制备的探针对文库进行筛选来分离目的基因。如植物抗病虫基因工程中常用的苏云金杆菌杀虫晶体蛋白基因(Bt基因)、豇豆胰蛋白酶抑制基因(Cp TI基因)、病毒外壳蛋白基因(CP基因)等。当其他植物的同类基因已分离到并且核苷酸序列保守性较高时,也可直接用这些已知的基因片段作探针对未克隆到该基因的植物基因文库进行筛选,也可分离到未知的新基因。 2、通过遗传表型分析 (1)基因标鉴法。该法是利用转座子或T-DNA插入植物的基因组中引起某一基因失活产生一些突变体,然后用相应转座子或T-DNA对突变体文库进行筛选,以选到的阳性克隆片段为探针,再筛选野生型植物因文库分离目的基因。如将一株带有功能的转位因子系统的植物与另一株在遗传上有差异的同种植物杂交,在杂交后代中筛选由于转位因子插入到某一特定基因序列中导致表型破坏或改变的突变株,用该纯合突变株构建基因文库,然后将转位因子用同位素标记作探针,从该文库中筛选出带有同源转位因子的目的基因。该法主要限于二倍体的自花授粉作物如玉米、金鱼草等。应用该法已分离出与玉米种子发育有关的Viviparious-1基因及与金鱼草花发育有关的一些基因等。 (2)激发子的寄主受体基因克隆技术。该技术是利用病菌无毒基因(avrgene)编氲募し⒆佑爰闹骺共』 虮嗦氲氖芴逯 浯嬖诓磺缀偷幕プ鞴叵担 圆≡ し⒆拥鞍孜 咚鞣掷牒涂寺〕鲆恍┘付≈士共』 颍 绶 延胛薅净 騛vr9对应的抗病基因cf9,与avrPto对应的抗病基因pto;拟南芥菜与avrRPS2对应的抗病基因rpS2等。 3、以图谱为基础的定位克隆技术 以图谱为基础的定位克隆技术在分离未知产物的基因方面有广阔的应用前景。该法的基本前提是基因定位,然后以紧密连锁的分子标记如RFLP等为起点,通过染色体步移逐步向目标基因靠近,最终克隆基因。其主要步骤包括:(1)将目标基因定位在高密度的分子标记连锁群上;(2)利用PFGE将连销标记的遗传图谱距转换成物理距离;(3)构建YAC文库,找到含连锁标记的YAC克隆,并通过克隆的排序获得目标基因的DNA片段;(4)通过转化和功能互补试验证实基因所在的DNA片
文档图位克隆原理及应用
位克隆技术的原理及其在分离玉米基因中的应用刘朝显2010.11.3 2 内容摘要图位克隆技术的基本原理1 图位克隆的技术环节 2 图位克隆在分离玉米基因中的应用 3 一. 图位克隆技术的基本原理 1. 图位克隆(Map-based cloning): 定位克隆(position cloning),1986 年首先由剑桥大学的Alan coulson 提出。正常遗传学 2. 基本原理:根据功能基因在基因组中都有相对较稳定的基因座,在利用分子标记技术对目的基因精细定位的基础上,用与目的基因紧密连锁的分子标记筛选DNA文库,通过染色体步移(chromosome walking)逼近目的基因或通过染色体登陆(chromosome landing)方法最后找到包含有该目的基因的克隆,最后经遗传转化试验证实目的基因功能。 3 3. 图位克隆技术的优越性与局限性优点:不需要事先了解目的基因的表达产物,这为克隆许多有重要经济价值的农作物基因提供了有效的手段,因为这些基因的产物大多都是未知的。缺点:基因组中的重复序列导致染色体步移困难,甚至将步移引入歧途。 4 一. 图位克隆技术的基本原理 4. 图位克隆示意图 5 一. 图位克隆技术的基本原理M1 M2 Gene 连锁标记的筛选M1 M2 Gene 初定位M3 M2 Gene 精细定位M3 M4 M5 M6 M7 M8 合成探针筛选基因组文库转基因功能验证BSA,NIL 300左右5000左右二. 图位克隆的技术环节 6 1.定位群体的构建⑴亲本选择原则:选择高度纯合,遗传差异大,DNA多态性丰富的亲本(实现基因精细定位的重要前提)可选用多个亲本进行多态性筛选⑵定位群体的组配:基因的定位是基于分离后代中交换单株出现的频率大小而实现的,因此组配一个遗传信息多群体大小适中的分离群体尤其重要。BC1,F2 非永久性群体群体类型RIL,DH,NIL 永久性群体 2. 初定位(玉米:100-350株) 近等基因系(near-isogenic line,NIL )法: 近等基因系是指几乎仅在目标性状上存在差异的两种基因型个体, 这可通过连续回交的途径获得。由于NILs 的遗传组成特点, 一般凡是能在近等基因系间揭示多态性的分子标记就极有可能位于目标基因的两翼附近。7 二. 图位克隆的技术环节Chromosome landing: a paradigm for map-based gene cloning in plants wi t h large genomes. Tanksley et al.1995 8 二. 图位克隆的技术环节集团分离分析法(bulked segregant analysis, BSA): 将分离群体中研究的目标性状根据其类型(如抗病、感病) 分成2组,将每组内一定数量的植株DNA等量混合,形成2个池,这2 个池仅在目标性状(如抗病性)上有差异。利用分子标记技术寻找2 个池的扩增谱带的差异,这种多态性极可能与目标基因连锁。9 Chromosome landing: a paradigm for map-based gene cloning in plants with large genomes. Tanksley et al.1995 10 M1 M2 二. 图位克隆的技术环节P1 P2 F1 P2 BC1 初定位示意图Recombinant 1 Recombinant 2 Marker I Marker II Target gene 3. 精细定位(玉米4000株)11 二. 图位克隆的技术环节MarkerI MarkerIII MarkerV MarkerVI MarkerIV MarkerII Target gene 上游交换单株下游交换单株 4. 构建高质量、容易操作的大片段基因组文库在基因的图位克隆技术中,高质量的基因组文库的构建也是克隆成功的关键。 YAC: 插入片段大(100-2000Kb),加速染色体步移; 嵌合情况严重,遗传不稳定,插入片段内部重排或者缺失,插入片段分离难,转化效率低。BAC:片段插入一般在150Kb左右。嵌合现象少,以大肠杆菌为寄主,转化效率高,提取容易,用途广泛。柯斯质粒文库:兼具了质粒和λ噬菌体两方面的特性插入片段最大可达45kb。 12 二. 图位克隆的技术环节 5. 鉴定目标基因利用与目标基因连锁的分子标记筛选基因组文库(PCR 反应或者菌落杂交),鉴定阳性克隆,并进行亚克隆测序,预测基因,确定候选基因。候选基因的确定:(1)比较候选基因序列在野生型与突变型之间的差异,确定在二者之间变异的cDNA 序列; (2)证实候选基因的时空表达模式与目标性状的表现相同; (3)转化候选基因,进行遗传互补实验,这是最直接、最终鉴定基因的方法。13 二. 图位克隆的技术环节三. 图位克隆在分离玉米基因中的应用1992 年应用图位克隆技术首先在拟南芥中成功分离基因ABI3和FAD基因。随后利用图位克隆技术又成功的从拟南芥、水稻、大麦、玉米和番茄等植物中克隆到了多个基因。随着测序技术的发展,拟南芥、黄瓜、水稻、玉米、高粱、大豆等植物的基因组测序已经完成,海量的SSR、SNP、In/Del、CAPS、dCAPS分子标记大大促进了图位克隆的速度。14 15 三. 图位克隆在分离玉米基因中的应用Vgt1 (Vegetative to generative transition 1) Toward positional cloning of Vgt1, a QTL controlling the transition from the vegetative to the reproductive phase in maize PMB. 2002 tga1 (teosinte glume architecture) The origin of the naked grains of maize. Nature. 2005 ramosa2 ramosa2 Encodes a LATERAL ORGAN BOUNDARY Domain Protein That Determines the Fate of Stem Cells in Branch Meristems of Maize
